Trong bối cảnh công nghệ sinh học đang phát triển mạnh mẽ, kỹ thuật Gibson Assembly đang nổi lên như một công cụ đột phá, giúp các nhà nghiên cứu dễ dàng thao tác với DNA mà không phụ thuộc vào các phương pháp truyền thống. Được phát triển bởi Daniel G. Gibson và cộng sự tại viện J. Craig Venter (JCVI – California, Mỹ) vào năm 2009 [1], kỹ thuật này đã được công bố trên tạp chí Nature Methods và nhanh chóng trở thành nền tảng trong kỹ thuật sinh học tổng hợp. Với khả năng lắp ráp DNA một cách liền mạch chỉ trong một phản ứng đẳng nhiệt, Gibson Assembly không chỉ đơn giản hóa quy trình mà còn mở ra nhiều ứng dụng tiềm năng, đặc biệt trong lĩnh vực công nghệ thực phẩm.
Gibson Assembly hoạt động dựa trên sự phối hợp của ba enzyme chính: 5' exonuclease, DNA polymerase và DNA ligase (Hình 1) [1]. Quy trình diễn ra ở nhiệt độ ổn định 50°C trong khoảng 15-60 phút. Đầu tiên, exonuclease loại bỏ nucleotide từ đầu 5' của các đoạn DNA, tạo ra các đầu nhô ra đơn sợi (overhangs) tại vùng chồng chéo (thường 20-40 bp). Các đầu này sau đó bắt cặp với nhau, polymerase giúp lấp đầy khoảng trống, và ligase nối kín các khoảng trống đó, hình thành phân tử DNA liền mạch. Phương pháp này vượt trội so với kỹ thuật enzyme cắt giới hạn truyền thống, vốn thường để lại "sẹo" trình tự và yêu cầu điều kiện nghiêm ngặt, dễ bị ảnh hưởng bởi methyl hóa DNA hoặc hoạt tính ngoài mục tiêu.
    |
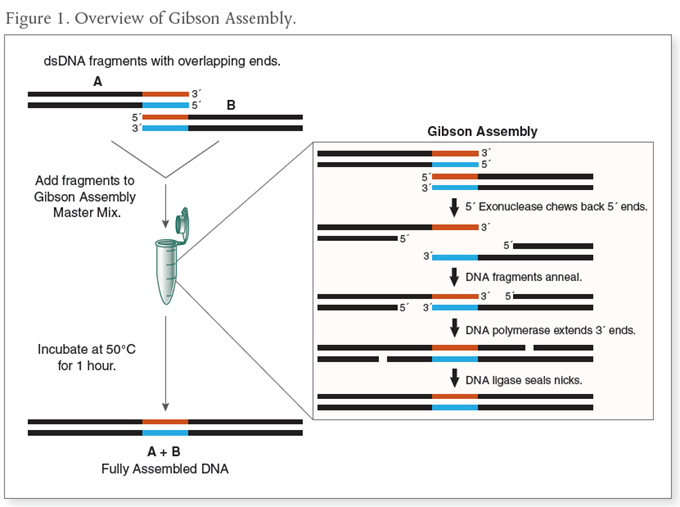 |
| Hình 1. Tổng quan về phản ứng xảy ra trong Gibson Assembly |
Một ứng dụng nổi bật của Gibson Assembly là trong cloning – tạo DNA tái tổ hợp. Kỹ thuật cho phép lắp ráp nhiều đoạn DNA chồng chéo mà không cần vị trí cắt enzyme giới hạn, giúp xây dựng vector biểu hiện hoặc plasmid một cách linh hoạt [2]. Ví dụ, các nhà khoa học tại JCVI đã sử dụng phương pháp này để lắp ráp bộ gen ty thể chuột (16,5 kb) từ 600 oligonucleotide 60-base [3], hoặc tổng hợp bộ gen Mycoplasma mycoides (1,08 Mbp) – bước ngoặt tạo ra tế bào tổng hợp đầu tiên [4]. Trong cloning, DNA có thể được chia thành các mảnh PCR chồng chéo, sau đó lắp ráp vào vector như pUC19 hoặc pTYB1, rồi chuyển nạp vào Escherichia coli để nhân bản. Điều này đặc biệt hữu ích cho việc chuyển gen từ sinh vật này sang sinh vật khác, như chuyển giao các con đường sinh tổng hợp các chất từ vi khuẩn sang nấm men (Hình 2).
    |
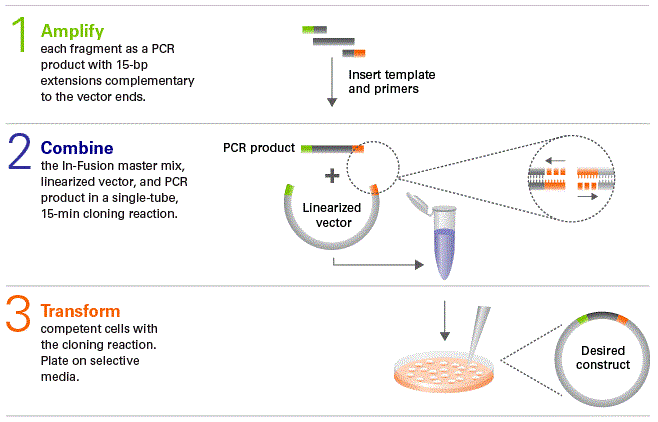 |
| Hình 2. Các bước thực hiện chuyển gen khi áp dụng phương pháp Gibson Assembly |
Bên cạnh đó, Gibson Assembly còn được ứng dụng nhiều trong việc tạo đột biến định hướng tại các vị trí xác dịnh. Bằng cách tích hợp thay đổi (thay thế, xóa, chèn nucleotide) vào primer PCR tại vùng chồng chéo, kỹ thuật cho phép chỉnh sửa DNA lớn một cách nhanh chóng [2]. Ví dụ, trong tổng hợp bộ gen M. mycoides, 16 mảnh DNA mô-đun đã được chỉnh sửa để khớp với trình tự mong muốn [4]. Với khả năng lắp ráp đồng thời nhiều mảnh (lên đến 8-12) (Hình 3), phương pháp có thể tạo 8 đột biến trên 80 kb DNA chỉ qua một phản ứng. Điều này giúp tối ưu hóa gen, như tăng cường biểu hiện protein hoặc cải thiện tính ổn định enzyme, mà không giới hạn bởi kích thước DNA [2].
    |
 |
| Hình 3. Phương pháp chèn 5 đoạn DNA vào vector bằng phương pháp Gibson Assembly |
Trong lĩnh vực công nghệ thực phẩm, Gibson Assembly đang mở ra xu hướng ứng dụng đầy hứa hẹn. Kỹ thuật hỗ trợ phát triển probiotic thế hệ mới bằng cách chỉnh sửa gen vi khuẩn lactic như Lactiplantibacillus plantarum, giúp tăng cường khả năng kháng bệnh hoặc sản xuất hợp chất có lợi (ví dụ: protein Elafin chống viêm) [5]. Một nghiên cứu gần đây trên tạp chí Vaccines (2023) đã sử dụng Gibson Assembly để tạo clone nhiễm của virus lở mồm long móng (FMDV) trên vector pKLS3, hỗ trợ sản xuất vaccine tùy chỉnh cho gia súc – góp phần bảo vệ an ninh thực phẩm [6]. Ngoài ra, phương pháp hỗ trợ lắp ráp các con đường sinh tổng hợp enzyme dùng trong thực phẩm (như amylase, protease) hoặc cải thiện giống cây trồng kháng sâu bệnh, tăng năng suất [7]. Trong sinh học tổng hợp, nó hỗ trợ tạo vi sinh vật sản xuất biofuel từ phụ phẩm nông nghiệp hoặc hợp chất tự nhiên như carotenoid, vitamin – hướng tới thực phẩm chức năng bền vững. Các nghiên cứu từ NEB và Thermo Fisher nhấn mạnh rằng Gibson Assembly giảm thời gian thí nghiệm, tăng độ chính xác, phù hợp cho sản xuất quy mô lớn trong công nghiệp thực phẩm [7].
Tuy nhiên, kỹ thuật vẫn có hạn chế như yêu cầu thiết kế primer chính xác (Hình 4), hiệu suất giảm với đoạn DNA ngắn (<200 bp) hoặc vùng chồng chéo có cấu trúc bậc hai. Để khắc phục, các phiên bản cải tiến như HiFi DNA Assembly đã được phát triển, sử dụng polymerase chính xác cao hơn [8].
    |
 |
| Hình 4. Yêu cầu thiết kế primer đối với phương pháp Gibson Assembly |
Tóm lại, Gibson Assembly không chỉ cách mạng hóa nghiên cứu sinh học mà còn mang lại lợi ích thiết thực cho công nghệ thực phẩm, từ cải thiện an toàn thực phẩm đến sản xuất bền vững. Với khả năng lắp ráp DNA linh hoạt và hiệu quả, kỹ thuật này đang mở ra những hướng ứng dụng mới mẻ trong sinh học tổng hợp, giúp các nhà khoa học thiết kế và chỉnh sửa gen một cách chính xác hơn. Là một công cụ nền tảng, Gibson Assembly hứa hẹn sẽ tiếp tục thúc đẩy các tiến bộ khoa học, góp phần giải quyết các thách thức toàn cầu trong lĩnh vực thực phẩm và y sinh.
TS. Lê Thiên Kim
Bộ môn Hóa sinh – Công nghệ sinh học thực phẩm
Tài liệu tham khảo
[1] Gibson, D. G., Young, L., Chuang, R.-Y., Venter, J. C., Hutchison, C. A., & Smith, H. O. (2009). Enzymatic assembly of DNA molecules up to several hundred kilobases. Nature Methods, 6(5), 343–345. https://doi.org/10.1038/nmeth.1318
[2] Gibson, D. G. (2011). Enzymatic assembly of overlapping DNA fragments. Methods in Enzymology, 498, 349–361. https://doi.org/10.1016/B978-0-12-385120-8.00015-2
[3] Gibson, D. G., Smith, H. O., Hutchison, C. A., Venter, J. C., & Merryman, C. (2010). Chemical synthesis of the mouse mitochondrial genome. Nature Methods, 7(11), 901–903. https://doi.org/10.1038/nmeth.1515
[4] Gibson, D. G., Benders, G. A., Andrews-Pfannkoch, C., Denisova, E. A., Baden-Tillson, H., Zaveri, J., Stockwell, T. B., Brownley, A., Thomas, D. W., Algire, M. A., Merryman, C., Young, L., Noskov, V. N., Glass, J. I., Venter, J. C., Hutchison, C. A., & Smith, H. O. (2010). Creation of a bacterial cell controlled by a chemically synthesized genome. Science, 329(5987), 52–56. https://doi.org/10.1126/science.1190719
[5] Kumar, A., Andersson, B., Barakat, M., & Impens, L. (2023). In vitro assembly of plasmid DNA for direct cloning in Lactiplantibacillus plantarum WCSF1. PLOS ONE, 18(2), e0281625. https://doi.org/10.1371/journal.pone.0281625
[6] Semkum, P., Chungjatupornchai, W., Sujjitjoon, J., Tangjatturon, N., Chatchaiphan, S., Bunnueang, N., Yamabhai, M., & Eiamphungporn, W. (2023). The application of the Gibson Assembly method in the production of two pKLS3 vector-derived infectious clones of foot-and-mouth disease virus. Vaccines, 11(6), 1111. https://doi.org/10.3390/vaccines11061111
[7] New England Biolabs. (n.d.). Gibson Assembly® Cloning Kit. Retrieved from https://www.neb.com/en/products/e5510-gibson-assembly-cloning-kit
[8] New England Biolabs. (n.d.). NEBuilder® HiFi DNA Assembly. Retrieved from https://www.neb.com/en-us/applications/cloning-and-synthetic-biology/dna-assembly-and-cloning/nebuilder-hifi-dna-assembly